Genomik
Genomics
Genomik, genomların yapısı, işlevi, gelişimi, haritalanması ve düzenlenmesine odaklanan disiplinler arası bir biyoloji alanıdır. Bir genom, bir organizmanın tüm genleri dahil olmak üzere eksiksiz DNA kümesidir. Bireysel genlerin ve bunların kalıtımdaki rollerinin incelenmesine atıfta bulunan genetiğin aksine, genomik bir organizmanın tüm genlerinin ve bunların karşılıklı ilişkilerinin kolektif karakterizasyonunu ve ölçülmesini amaçlamaktadır. ve organizma üzerindeki etkisi. Genler, enzimlerin ve haberci moleküllerin yardımıyla protein üretimini yönlendirebilir. Sırasıyla, proteinler, organlar ve dokular gibi vücut yapılarını oluşturur, kimyasal reaksiyonları kontrol eder ve hücreler arasında sinyaller taşır. Genomik ayrıca, tüm genomların işlevini ve yapısını bir araya getirmek ve analiz etmek için yüksek verimli DNA dizileme ve biyoinformatik kullanımları yoluyla genomların dizilenmesini ve analizini içerir. Genomikteki gelişmeler, beyin gibi en karmaşık biyolojik sistemlerin bile anlaşılmasını kolaylaştırmak için keşfe dayalı araştırma ve sistem biyolojisinde bir devrimi tetikledi.
Alan ayrıca intragenomik (genom içinde) fenomenlerle ilgili çalışmaları da içerir. epistasis (bir genin diğerine etkisi), pleiotropi (birden fazla özelliği etkileyen bir gen), heterosis (hibrit canlılık) ve genom içindeki lokuslar ve aleller arasındaki diğer etkileşimler gibi.
İçindekiler
Tarih
Etimoloji
Yunancadan ΓΕΝ gen , "gen" (gama, epsilon, nu, epsilon) "olmak, oluşturma, yaratma, doğum "ve sonraki varyantlar: şecere, genesis, genetik, genetik, genomere, genotip, cins vb. genom kelimesi (Almanca Genom 'den, Hans Winkler'a atfedilen) 1926 gibi erken bir tarihte İngilizce kullanımdaydı, genomik terimi, Jackson Laboratuvarı'nda (Bar Harbor, Maine) bir genetikçi olan Tom Roderick tarafından düzenlenen bir toplantıda bira üzerine icat edildi. ben n Maryland 1986'da insan genomunun haritalanmasında.
Erken sıralama çabaları
Rosalind Franklin'in DNA'nın sarmal yapısını onaylamasının ardından James D. Watson ve Francis Crick'in DNA'nın 1953'teki yapısı ve Fred Sanger'in 1955'te insülinin Amino asit dizisini yayınlaması, nükleik asit dizilimi erken moleküler biyologların başlıca hedefi haline geldi. 1964'te Robert W. Holley ve meslektaşları, alanin transfer RNA'nın ribonükleotid dizisi olan şimdiye kadar belirlenmiş ilk nükleik asit dizisini yayınladılar. Bu çalışmayı genişleten Marshall Nirenberg ve Philip Leder, genetik kodun üçlü yapısını ortaya çıkardı ve deneylerinde 64 kodonun 54'ünün dizisini belirleyebildiler. 1972'de, Walter Fiers ve Ghent Üniversitesi Moleküler Biyoloji Laboratuvarındaki ekibi (Belçika, Ghent) bir genin dizisini ilk belirleyenlerdi: Bakteriyofaj MS2 kaplama proteini için gen. Fiers'ın grubu, sırasıyla 1976 ve 1978'de bakteriyofaj MS2-RNA'nın (genomu 3569 baz çiftinde sadece dört geni kodlayan) ve Simian virüsü 40'ın tam nükleotid dizisini belirleyerek MS2 kaplama protein çalışmalarını genişletti.
DNA dizileme teknolojisi geliştirildi
Frederick Sanger ve meslektaşları, insülinin amino asit dizisi üzerindeki çığır açan çalışmalarına ek olarak, kapsamlı genom dizileme projeleri. 1975 yılında, o ve Alan Coulson, Artı ve Eksi tekniği adını verdiği radyo etiketli nükleotidlerle DNA polimeraz kullanan bir sıralama prosedürü yayınladılar. Bu, tanımlanmış 3 'uçlu kısa oligonükleotidler üreten yakından ilişkili iki yöntemi içeriyordu. Bunlar, bir poliakrilamid jel (poliakrilamid jel elektroforezi olarak adlandırılır) üzerinde elektroforez ile parçalanabilir ve otoradyografi kullanılarak görselleştirilebilir. Prosedür tek seferde 80 nükleotide kadar sıralayabiliyordu ve büyük bir gelişmeydi, ancak yine de çok zahmetliydi. Bununla birlikte, 1977'de grubu, tek sarmallı bakteriyofaj φX174'ün 5,386 nükleotidinin çoğunu sıralamayı başardı ve ilk tam sekanslı DNA bazlı genomu tamamladı. Plus and Minus yönteminin iyileştirilmesi, DNA dizileme, genom haritalama, veri depolama ve biyoinformatik analiz tekniklerinin temelini oluşturan zincir sonlandırma veya Sanger yöntemiyle (aşağıya bakın) sonuçlandı. en yaygın olarak sonraki çeyrek yüzyıllık araştırmalarda kullanılmaktadır. Aynı yıl Harvard Üniversitesi'nden Walter Gilbert ve Allan Maxam, DNA dizilemesinin Maxam-Gilbert yöntemini ( kimyasal yöntem olarak da bilinir) bağımsız olarak geliştirdi ve bilinen bazlarda DNA'nın tercihli bölünmesini içeren, daha az verimli yöntem. Gilbert ve Sanger, nükleik asitlerin dizilenmesindeki çığır açan çalışmaları için 1980 Nobel Kimya Ödülü'nün yarısını Paul Berg (rekombinant DNA) ile paylaştı.
Tam genomlar
Bu teknolojilerin ortaya çıkışı, genom dizileme projelerinin kapsamı ve tamamlanma hızında hızlı bir yoğunlaşma ile sonuçlandı. Ökaryotik bir organelin ilk tam genom dizisi, insan mitokondrisi (16.568 bp, yaklaşık 16.6 kb) 1981'de ve ilk kloroplast genomları 1986'da rapor edildi. 1992'de, ilk ökaryotik kromozom, bira mayasının kromozom III'ü Saccharomyces cerevisiae (315 kb) sekanslandı. Sıralanacak ilk serbest yaşayan organizma 1995'te Haemophilus influenzae (1.8 Mb) 'dendi. Ertesi yıl Kuzey Amerika, Avrupa ve Japonya'daki laboratuarlardan bir araştırmacı konsorsiyumu bir ökaryotun ilk tam genom dizisi, S. cerevisiae (12.1 Mb) ve o zamandan beri genomlar katlanarak artan bir hızda dizilenmeye devam ediyor. Ekim 2011 itibariyle, tam sekanslar şu şekildedir: 2.719 virüs, 1.115 arke ve bakteri ve yaklaşık yarısı mantar olan 36 ökaryot.
Genomları tamamen dizilenmiş mikroorganizmaların çoğu sorunludur. Haemophilus influenzae gibi patojenler, mikrobiyal çeşitliliğin genişliği ile karşılaştırıldığında filogenetik dağılımlarında belirgin bir önyargıya neden olur. Sıralanan diğer türlerin çoğu, iyi çalışılmış model organizmalar oldukları veya iyi modeller olma sözü verdikleri için seçildi. Maya ( Saccharomyces cerevisiae ) uzun süredir ökaryotik hücre için önemli bir model organizma iken, meyve sineği Drosophila melanogaster çok önemli bir araç olmuştur (özellikle erken moleküler genetik). Caenorhabditis elegans solucanı, çok hücreli organizmalar için sıklıkla kullanılan basit bir modeldir. Zebra balığı Brachydanio rerio moleküler düzeyde birçok gelişim araştırması için kullanılır ve Arabidopsis thaliana bitkisi çiçekli bitkiler için model bir organizmadır. Japon kirpi balığı ( Takifugu rubripes ) ve benekli yeşil kirpi balığı ( Tetraodon nigroviridis ), çoğu türe kıyasla çok az kodlamayan DNA içeren küçük ve kompakt genomları nedeniyle ilginçtir. . Memeli köpeği ( Canisiliaris ), kahverengi sıçan ( Rattus norvegicus ), fare ( Mus musculus ) ve şempanze ( Pan troglodytes ) tıbbi araştırmalarda önemli model hayvanlardır.
İnsan genomunun kaba bir taslağı 2001 yılının başlarında İnsan Genomu Projesi tarafından tamamlandı ve büyük bir hayranlık uyandırdı. 2003 yılında tamamlanan bu proje, belirli bir kişi için tüm genomu sıraladı ve 2007'ye kadar bu dizinin "bittiği" ilan edildi (20.000 bazda birden az hata ve tüm kromozomlar bir araya getirildi). O zamandan bu yana geçen yıllarda, kısmen Ekim 2012'de 1.092 genomun dizilişini duyuran 1000 Genom Projesi'nin himayesinde birçok başka bireyin genomları dizilenmiştir. Bu projenin tamamlanması, çok daha fazlasının geliştirilmesiyle mümkün olmuştur. verimli sıralama teknolojileri ve büyük bir uluslararası işbirliğinden önemli biyoinformatik kaynakların taahhüt edilmesini gerektirdi. İnsan genomik verilerinin sürekli analizinin, insan toplumları için derin politik ve sosyal yansımaları vardır.
"Omik" devrimi
İngilizce dilindeki neologism omics, gayri resmi olarak bir çalışma alanını ifade eder. genomik, proteomik veya metabolomik gibi -omik ile biten biyoloji. İlgili son ek -ome, sırasıyla genom, proteom veya metabolom gibi bu tür alanların çalışma nesnelerini ele almak için kullanılır. Moleküler biyolojide kullanılan -ome son eki, bir tür bütünlüğe atıfta bulunur; Benzer şekilde omik, genel olarak büyük, kapsamlı biyolojik veri setlerinin incelenmesine gönderme yapmaya başlamıştır. Terimin kullanımındaki artış, bazı bilim adamlarının (Jonathan Eisen, diğerleri arasında) aşırı satıldığını iddia etmesine yol açsa da, bu terimin tüm bileşenlerinin tam veya neredeyse eksiksiz çeşitliliğinin nicel analizine yönelik yönelimdeki değişikliği yansıtır. bir sistem. Örneğin, ortakyaşam çalışmalarında, bir zamanlar tek bir gen ürünü üzerinde çalışmakla sınırlı olan araştırmacılar artık birkaç biyolojik molekül türünün toplam tamamlayıcısını aynı anda karşılaştırabilir.
Genom analizi
Bir organizma seçildikten sonra, genom projeleri üç bileşen içerir: DNA'nın sıralanması, orijinal kromozomun bir temsilini oluşturmak için bu dizinin bir araya getirilmesi ve bu temsilin ek açıklaması ve analizi.
Sıralama
Tarihsel olarak sekanslama, sıralama merkezlerinde , merkezi tesislerde (yılda düzinelerce terabazı sıralayan Ortak Genom Enstitüsü gibi büyük bağımsız kurumlardan, araştırma içeren yerel moleküler biyoloji temel tesislerine kadar) yapıldı. pahalı enstrümantasyon ve gerekli teknik desteğe sahip laboratuvarlar. Bununla birlikte, sıralama teknolojisi gelişmeye devam ederken, yeni nesil etkili, hızlı geri dönüşlü masa üstü sıralayıcılar, ortalama bir akademik laboratuvara ulaşmıştır. Genel olarak, genom dizileme yaklaşımları iki geniş kategoriye ayrılır: shotgun ve yüksek verimli (veya yeni nesil ) dizileme.
Shotgun dizileme, tüm kromozomlar dahil olmak üzere 1000 baz çiftinden uzun DNA dizilerinin analizi için tasarlanmış bir dizileme yöntemidir. Bir av tüfeğinin hızla genişleyen, yarı rastgele ateşleme modeli ile analoji olarak adlandırılır. Jel elektroforez dizilimi yalnızca oldukça kısa diziler için kullanılabildiğinden (100-1000 baz çifti), daha uzun DNA dizilerinin rastgele küçük bölümlere bölünmesi ve ardından okumalar elde etmek için dizilenmesi gerekir. Hedef DNA için birden fazla örtüşen okuma, bu parçalanma ve dizilemenin birkaç turu gerçekleştirilerek elde edilir. Bilgisayar programları daha sonra farklı okumaların üst üste gelen uçlarını kullanarak bunları sürekli bir sıra halinde bir araya getirir. Shotgun dizileme, belirli bir nükleotidin yeniden yapılandırılmış dizide temsil edilmesini sağlamak için aşırı örnekleme gerektiren rastgele bir örnekleme sürecidir; Bir genomun aşırı örneklendiği ortalama okuma sayısı kapsam olarak adlandırılır.
Tarihinin çoğunda, av tüfeği diziliminin altında yatan teknoloji klasik zincir sonlandırma yöntemi veya "Sanger yöntemi" idi. bu, in vitro DNA replikasyonu sırasında DNA polimeraz tarafından zincir sonlandırıcı dideoksinükleotidlerin seçici olarak dahil edilmesine dayanır. Son zamanlarda, özellikle büyük ölçekli otomatik genom analizleri için, shotgun sekanslamanın yerini yüksek verimli sıralama yöntemleri almıştır. Bununla birlikte, Sanger yöntemi, özellikle daha küçük ölçekli projeler ve özellikle uzun bitişik DNA dizisi okumaları (> 500 nükleotid) elde etmek için geniş kullanımda kalmaktadır. Zincir sonlandırma yöntemleri, tek sarmallı bir DNA şablonu, bir DNA primeri, bir DNA polimeraz, normal deoksinükleosid trifosfatlar (dNTP'ler) ve DNA sarmalı uzamasını sonlandıran modifiye nükleotidler (dideoksiNTP'ler) gerektirir. Bu zincir sonlandırıcı nükleotidler, iki nükleotid arasında bir fosfodiester bağının oluşması için gereken bir 3'-OH grubundan yoksundur ve bir ddNTP eklendiğinde DNA polimerazın DNA'nın uzamasını durdurmasına neden olur. DdNTP'ler, DNA sıralayıcılarında saptama için radyoaktif olarak veya floresan olarak etiketlenebilir. Tipik olarak, bu makineler günde 48 çalışmaya kadar tek bir grupta (çalışmada) 96 adede kadar DNA örneğini sıralayabilir.
Düşük maliyetli dizileme için yüksek talep, yüksek verimli dizileme geliştirilmesine yol açmıştır. dizileme sürecini paralelleştiren, aynı anda binlerce veya milyonlarca dizi üreten teknolojiler. Yüksek verimli sıralama, standart boya sonlandırıcı yöntemlerle mümkün olandan daha fazla DNA dizileme maliyetini düşürmeyi amaçlamaktadır. Ultra yüksek verimli dizilemede, 500.000'e kadar sentez yoluyla dizileme işlemi paralel olarak çalıştırılabilir.
Illumina boya sıralama yöntemi, tersinir boya sonlandırıcılara dayanır ve 1996 yılında, Pascal Mayer ve Laurent Farinelli tarafından Cenevre Biyomedikal Araştırma Enstitüsü. Bu yöntemde, DNA molekülleri ve primerler önce bir slayta eklenir ve polimeraz ile amplifiye edilir, böylece başlangıçta "DNA kolonileri" oluşturulan yerel klonal koloniler oluşturulur. Diziyi belirlemek için dört tip tersinir sonlandırıcı baz (RT-bazları) eklenir ve dahil edilmeyen nükleotidler yıkanır. Pyrosequencing'den farklı olarak, DNA zincirleri bir seferde bir nükleotid genişletilir ve görüntü edinimi gecikmeli bir anda gerçekleştirilebilir, bu da çok büyük DNA kolonileri dizilerinin tek bir kameradan alınan sıralı görüntülerle yakalanmasına izin verir. Enzimatik reaksiyonun ve görüntü yakalamanın ayrılması, optimum verim ve teorik olarak sınırsız sıralama kapasitesi sağlar; Optimal bir konfigürasyonla, enstrümanın nihai verimi yalnızca kameranın A / D dönüşüm oranına bağlıdır. Kamera, floresan olarak etiketlenmiş nükleotidlerin görüntülerini alır ve ardından, boya, terminal 3 'bloker ile birlikte kimyasal olarak DNA'dan çıkarılır ve bir sonraki döngüye izin verilir.
Alternatif bir yaklaşım olan iyon yarı iletken dizileme, standart DNA replikasyon kimyasına dayanır. Bu teknoloji, bir baz her eklendiğinde bir hidrojen iyonunun salınımını ölçer. Şablon DNA içeren bir mikro kuyu, tek bir nükleotid ile doldurulur, eğer nükleotid şablon ipliğe tamamlayıcı ise, bu dahil edilecek ve bir hidrojen iyonu salılacaktır. Bu sürüm, bir ISFET iyon sensörünü tetikler. Şablon dizide bir homopolimer varsa, birden fazla nükleotid tek bir taşma döngüsüne dahil edilecektir ve tespit edilen elektrik sinyali orantılı olarak daha yüksek olacaktır.
Montaj
Sıra montajı hizalamaya atıfta bulunur ve orijinal diziyi yeniden yapılandırmak için çok daha uzun bir DNA dizisinin parçalarını birleştirmek. Mevcut DNA sıralama teknolojisi, tüm genomları sürekli bir dizi olarak okuyamadığından, kullanılan teknolojiye bağlı olarak 20 ila 1000 baz arasında küçük parçaları okuduğundan bu gereklidir. PacBio veya Oxford Nanopore gibi üçüncü nesil dizileme teknolojileri rutin olarak> 10 kb uzunlukta dizileme okumaları üretir; ancak, yaklaşık yüzde 15 gibi yüksek bir hata oranına sahiptirler. Tipik olarak, okuma adı verilen kısa parçalar, genomik DNA veya gen transkriptlerinin (EST) sekanslamasından elde edilir.
Birleştirme, genel olarak iki yaklaşıma ayrılabilir: de novo montaj, Geçmişte dizilenenlere benzemeyen genomlar ve yakından ilişkili bir organizmanın mevcut dizisini montaj sırasında referans olarak kullanan karşılaştırmalı derleme. Karşılaştırmalı birleştirme ile karşılaştırıldığında, de novo montaj hesaplama açısından zordur (NP-zor), bu da onu kısa süreli NGS teknolojileri için daha az elverişli hale getirir. de novo montaj paradigması içinde, montaj için iki temel strateji vardır, Euler yol stratejileri ve örtüşme-yerleşim-fikir birliği (OLC) stratejileri. OLC stratejileri nihayetinde NP açısından zor bir problem olan bir örtüşme grafiği aracılığıyla bir Hamilton yolu yaratmaya çalışır. Euler yol stratejileri sayısal olarak daha izlenebilirdir çünkü bir deBruijn grafiği aracılığıyla Euler yolu bulmaya çalışırlar.
Bitmiş genomlar, her replikonu temsil eden belirsizlikler içermeyen tek bir bitişik diziye sahip olarak tanımlanır.
Ek açıklama
DNA sekansı düzeneğinin tek başına ek analiz olmaksızın çok az değeri vardır. Genom ek açıklaması, biyolojik bilgileri dizilere ekleme sürecidir ve üç ana adımdan oluşur:
- genomun proteinleri kodlamayan kısımlarını tanımlama
- üzerindeki öğeleri tanımlama genom, gen tahmini adı verilen bir süreçtir ve
- biyolojik bilgilerin bu öğelere eklenmesi.
Otomatik açıklama araçları bu adımları silico'da , insan uzmanlığını ve potansiyel deneysel doğrulamayı içeren manuel ek açıklamanın (diğer bir deyişle iyileştirme) aksine. İdeal olarak, bu yaklaşımlar aynı açıklama ardışık düzeninde birlikte var olur ve birbirini tamamlar (ayrıca aşağıya bakın).
Geleneksel olarak, temel açıklama düzeyi, benzerlikleri bulmak için BLAST kullanmak ve ardından homologlara dayalı genomları açıklama yapmaktır. . Daha yakın zamanlarda, açıklama platformuna ek bilgiler eklenmiştir. Ek bilgiler, manuel açıklayıcıların aynı not verilen genler arasındaki uyuşmazlıkları çözmesine izin verir. Bazı veritabanları, Subsystems yaklaşımları aracılığıyla genom ek açıklamaları sağlamak için genom bağlam bilgilerini, benzerlik puanlarını, deneysel verileri ve diğer kaynakların entegrasyonlarını kullanır. Diğer veritabanları (örneğin Ensembl), hem küratörlü veri kaynaklarına hem de otomatik genom açıklama ardışık düzenlerinde bir dizi yazılım aracına güvenir. Yapısal açıklama genomik elemanların, özellikle ORF'lerin ve bunların lokalizasyonunun veya gen yapısının tanımlanmasından oluşur. İşlevsel açıklama , biyolojik bilgilerin genomik öğelere eklenmesinden oluşur.
Ardışık düzenleri ve veritabanlarını sıralamak
Yeniden üretilebilirlik ve ilişkili büyük miktarda verinin verimli yönetimi ihtiyacı genom projeleriyle, hesaplamalı ardışık düzenlerin genomikte önemli uygulamaları olduğu anlamına gelir.
Araştırma alanları
Fonksiyonel genomik
İşlevsel genomik, gen (ve protein) işlevlerini ve etkileşimlerini tanımlamak için genomik projeler (genom dizileme projeleri gibi) tarafından üretilen çok sayıda veriden yararlanmaya çalışan bir moleküler biyoloji alanıdır. Fonksiyonel genomik, DNA dizisi veya yapıları gibi genomik bilginin statik yönlerinin aksine, gen transkripsiyonu, translasyonu ve protein-protein etkileşimleri gibi dinamik yönlere odaklanır. İşlevsel genomik, genler, RNA transkriptleri ve protein ürünleri seviyelerinde DNA'nın işlevi hakkındaki soruları yanıtlamaya çalışır. Fonksiyonel genomik çalışmalarının temel bir özelliği, bu sorulara genom çapında yaklaşımıdır ve genellikle daha geleneksel bir "gen-gen" yaklaşımı yerine yüksek verimli yöntemleri içerir.
Genomik biliminin ana dallarından biri şudur. Hala çeşitli organizmaların genomlarının sıralanmasıyla ilgileniyor, ancak tam genomların bilgisi, esas olarak çeşitli koşullar sırasında gen ekspresyon modelleriyle ilgili olan işlevsel genomik alanı için olasılık yarattı. Buradaki en önemli araçlar mikro diziler ve biyoinformatiktir.
Yapısal genomik
Yapısal genomik, belirli bir genom tarafından kodlanan her proteinin 3 boyutlu yapısını tanımlamaya çalışır. Bu genom tabanlı yaklaşım, deneysel ve modelleme yaklaşımlarının bir kombinasyonu ile yüksek verimli bir yapı belirleme yöntemine izin verir. Yapısal genomik ile geleneksel yapısal tahmin arasındaki temel fark, yapısal genomiğin belirli bir proteine odaklanmak yerine, genom tarafından kodlanan her proteinin yapısını belirlemeye çalışmasıdır. Tam genom dizileri mevcut olduğunda, yapı tahmini, deneysel ve modelleme yaklaşımlarının bir kombinasyonu yoluyla daha hızlı yapılabilir, çünkü özellikle çok sayıda dizilenmiş genomun ve önceden çözülmüş protein yapılarının mevcudiyeti, bilim adamlarının daha önce çözülmüş yapıların yapıları üzerindeki protein yapısını modellemesine izin verir homologlar. Yapısal genomik, genomik dizileri kullanan deneysel yöntemler veya bilinen yapıdaki bir proteine dizilim veya yapısal homolojiye dayalı modelleme tabanlı yaklaşımlar veya homolojisi olmayan bir protein için kimyasal ve fiziksel ilkelere dayanan çok sayıda yapı belirleme yaklaşımını içerir. bilinen herhangi bir yapı. Geleneksel yapısal biyolojinin aksine, yapısal bir genomik çabasıyla bir protein yapısının belirlenmesi, protein işlevi ile ilgili herhangi bir şey bilinmeden önce (her zaman değil) sıklıkla gelir. Bu, yapısal biyoinformatikte yeni zorluklar doğurur, yani protein işlevini 3 boyutlu yapısından belirleme.
Epigenomics
Epigenomics, bir hücrenin genetik materyali üzerindeki epigenetik modifikasyonların eksiksiz bir çalışmadır. , epigenom olarak bilinir. Epigenetik modifikasyonlar, bir hücrenin DNA'sı veya histonları üzerinde, DNA sekansını değiştirmeden gen ekspresyonunu etkileyen tersine çevrilebilir modifikasyonlardır (Russell 2010 s. 475). En karakteristik epigenetik modifikasyonlardan ikisi, DNA metilasyonu ve histon modifikasyonudur. Epigenetik modifikasyonlar gen ekspresyonunda ve regülasyonunda önemli bir rol oynar ve farklılaşma / gelişme ve tümörijenez gibi çok sayıda hücresel süreçte yer alır. Küresel düzeyde epigenetik çalışması, ancak yakın zamanda genomik yüksek verimli tahlillerin uyarlanmasıyla mümkün olmuştur.
Metagenomik
Metagenomik, metagenomların , doğrudan çevresel örneklerden elde edilen genetik materyal. Geniş alan ayrıca çevresel genomik, ekojenomik veya topluluk genomiği olarak da adlandırılabilir. Geleneksel mikrobiyoloji ve mikrobiyal genom dizilimi, kültürlenmiş klonal kültürlere dayanırken, erken çevresel gen dizilimi, doğal bir örnekte bir çeşitlilik profili oluşturmak için spesifik genleri (genellikle 16S rRNA geni) klonladı. Bu tür çalışmalar, mikrobiyal biyoçeşitliliğin büyük çoğunluğunun ekime dayalı yöntemlerle gözden kaçırıldığını ortaya çıkardı. Yakın zamanda yapılan araştırmalar, örneklenmiş toplulukların tüm üyelerinden tüm genlerin büyük ölçüde tarafsız örneklerini almak için "shotgun" Sanger dizilemesi veya büyük ölçüde paralel piroz dizileme kullanır. Metagenomik, mikroskobik yaşamın önceden gizli olan çeşitliliğini ortaya çıkarma gücü nedeniyle, tüm yaşayan dünyanın anlayışında devrim yaratma potansiyeline sahip mikrobiyal dünyayı görüntülemek için güçlü bir mercek sunar.
Model sistemler
Bakteriyofajlar, bakteriyel genetik ve moleküler biyolojide önemli bir rol oynamış ve oynamaya devam etmektedir. Tarihsel olarak, gen yapısını ve gen düzenlemesini tanımlamak için kullanıldılar. Ayrıca dizilenecek ilk genom bir bakteriyofajdı. Bununla birlikte, bakteriyofaj araştırması, bakteriyel genomiklerin açıkça hakim olduğu genomik devrimine öncülük etmedi. Bakteriyofaj genomları üzerine yapılan çalışmalar çok yakın zamanda öne çıkarak araştırmacıların faj evriminin altında yatan mekanizmaları anlamalarını sağladı. Bakteriyofaj genom sekansları, izole edilmiş bakteriyofajların doğrudan sekanslanması yoluyla elde edilebilir, ancak mikrobiyal genomların bir parçası olarak da türetilebilir. Bakteriyel genomların analizi, önemli miktarda mikrobiyal DNA'nın profilaktik dizilerden ve peygamberlik benzeri elementlerden oluştuğunu göstermiştir. Bu dizilerin ayrıntılı bir veri tabanı madenciliği, kehanetlerin bakteriyel genomu şekillendirmedeki rolüne dair içgörü sağlar: Genel olarak, bu yöntem bilinen birçok bakteriyofaj grubunu doğruladı ve bu, bakteriyel genomlardan alınan peygamberlerin ilişkilerini tahmin etmek için yararlı bir araç haline getirdi. p> Şu anda, toplam genom dizisinin mevcut olduğu 24 siyanobakteri vardır. Bu siyanobakterilerin 15'i deniz ortamından gelmektedir. Bunlar altı Prochlorococcus suşu, yedi deniz Synechococcus suşu, Trichodesmium erythraeum IMS101 ve Crocosphaera watsonii WH8501'dir. Çeşitli çalışmalar, bu dizilerin deniz siyanobakterilerinin önemli ekolojik ve fizyolojik özelliklerini çıkarmak için nasıl çok başarılı bir şekilde kullanılabileceğini göstermiştir. Bununla birlikte, şu anda devam etmekte olan daha birçok genom projesi vardır, bunların arasında Prochlorococcus ve deniz Synechococcus izolatları, Acaryochloris ve Prochloron , N2-sabitleyici ipliksi siyanobakteriler Nodularia spumigena , Lyngbya aestuarii ve Lyngbya majuscula ve ayrıca deniz siyanobakerlerine bulaşan bakteriyofajlar. Böylelikle, artan genom bilgisine, karşılaştırmalı bir yaklaşım uygulayarak küresel sorunları ele almak için daha genel bir şekilde yararlanılabilir. Bu alandaki ilerlemenin bazı yeni ve heyecan verici örnekleri, düzenleyici RNA'lar için genlerin belirlenmesi, fotosentezin evrimsel kökenine ilişkin içgörüler veya yatay gen transferinin analiz edilen genomlara katkısının tahminidir.
Genomik uygulamaları
Genomik, tıp, biyoteknoloji, antropoloji ve diğer sosyal bilimler dahil olmak üzere birçok alanda uygulama sağlamıştır.
Genomik tıp
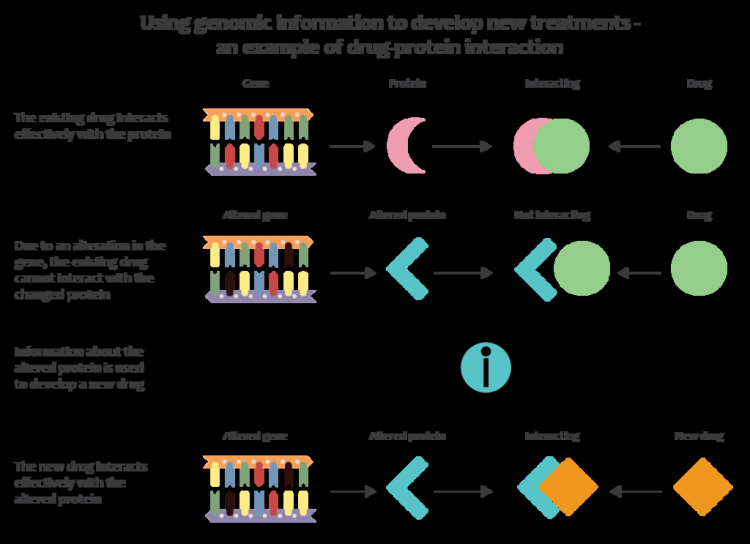
Yeni nesil genomik teknolojiler, klinisyenlerin ve biyomedikal araştırmacıların büyük çalışma popülasyonlarında toplanan genomik veri miktarını önemli ölçüde artırmasına olanak tanır. Hastalık araştırmalarında birçok tür veriyi genomik verilerle bütünleştiren yeni bilişim yaklaşımlarıyla birleştirildiğinde, bu, araştırmacıların ilaç tepkisinin ve hastalığın genetik temellerini daha iyi anlamasına olanak tanır. Genomu tıbba uygulamak için ilk çabalar, bir insan genomunun tıbbi yorumu için ilk araçları geliştiren Euan Ashley liderliğindeki bir Stanford ekibinin çalışmalarını içeriyordu. Örneğin, Hepimiz araştırma programı, hassas tıp araştırma platformunun kritik bir bileşeni olmak için 1 milyon katılımcıdan genom dizisi verilerini toplamayı amaçlamaktadır.
Sentetik biyoloji ve biyomühendislik
Genomik bilginin büyümesi, sentetik biyolojinin giderek daha karmaşık uygulamalarını mümkün kılmıştır. 2010 yılında J. Craig Venter Enstitüsü'ndeki araştırmacılar, Mycoplasma genitalium genomundan türetilen, kısmen sentetik bir bakteri türü olan Mycoplasma laboratorium 'un yaratıldığını duyurdular.
Koruma genomiği
Koruma uzmanları, bir popülasyonun genetik çeşitliliği veya bir bireyin resesif için heterozigot olup olmadığı gibi türlerin korunmasında anahtar olan genetik faktörleri daha iyi değerlendirmek için genomik dizileme ile toplanan bilgileri kullanabilir. kalıtsal genetik bozukluk. Koruma uzmanları, evrimsel süreçlerin etkilerini değerlendirmek ve belirli bir popülasyondaki varyasyon kalıplarını tespit etmek için genomik verileri kullanarak, standart genetik yaklaşımlarla adreslenmemiş olanlar kadar bilinmeyen birçok değişken olmadan belirli bir türe yardımcı olacak planlar formüle edebilir.
Gugi Health: Improve your health, one day at a time!


